Identyfikacja klucza elementu przestawnego

obraz:
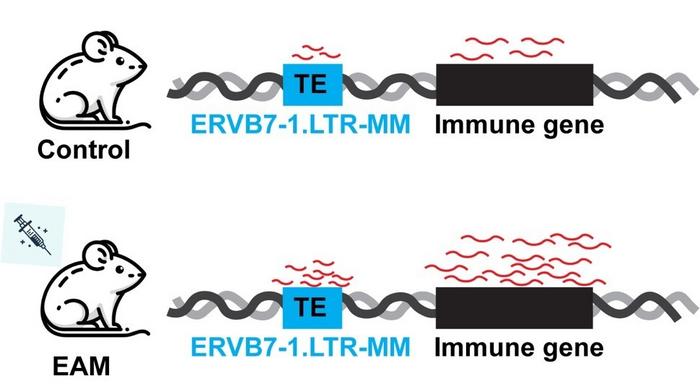
Ten schemat ilustruje obserwację rozległej aktywacji genów odpornościowych i elementów transpozycyjnych (TE) u myszy z EAM
pogląd więcej
Źródło: Sixing Chen
Historycznie uważane za pasożyty genomowe, elementy transpozycyjne (TE) zostały obecnie uznane za istotne czynniki wpływające na tożsamość i funkcjonowanie komórek, zwłaszcza w regulacji odporności.
Genomy ssaków zawierają ogromną liczbę TE. Różnorodność i obfitość tych elementów wpływa na strukturę, funkcję i ewolucję genomu. Wpływają na sieci regulacyjne genów, zmieniając miejsca wiązania czynników transkrypcyjnych i tworząc nowe działania wzmacniające. Coraz częściej pojawiają się dowody podkreślające kluczową rolę TE w różnych chorobach, zwłaszcza w modulowaniu odporności. Jednakże w kontekście zapalenia mięśnia sercowego zauważalny jest brak skupienia się na wpływie TE, co podkreśla potencjalny obszar badań, który mógłby dostarczyć nowych informacji na temat mechanizmów molekularnych powodujących tę chorobę serca.
W badaniu opublikowanym w czasopiśmie KeAi Rozmnażanie i hodowlazespół naukowców z Hunan Normal University wykorzystał dane dotyczące RNA-Seq i jednokomórkowych RNA-Seq w celu zidentyfikowania kluczowych TE związanych z zapaleniem mięśnia sercowego.
Zespół wykorzystał publicznie dostępne bazy danych do zbadania roli TE w zapaleniu mięśnia sercowego. Przeanalizowano dane dotyczące sekwencji RNA i dane dotyczące sekwencjonowania pojedynczych komórek, ze szczególnym uwzględnieniem mysiego modelu eksperymentalnego autoimmunologicznego zapalenia mięśnia sercowego (EAM). Analiza RNA-Seq ujawniła znaczną regulację w górę szeregu genów odpornościowych w tkance serca.
„Pogłębiliśmy badania, wykorzystując sekwencjonowanie pojedynczych komórek komórek odpornościowych serca, i zidentyfikowaliśmy specyficzną ekspresję pewnych elementów transpozycyjnych (TE) w różnych typach komórek odpornościowych serca” – mówi pierwszy autor badania, Sixing Chen. „Zaobserwowaliśmy ogólny wzrost ekspresji ERVB7-1”.
Transpozon LTR-MM w różnych komórkach w modelu EAM sugeruje powszechny wpływ tego transpozonu na odpowiedź immunologiczną w kontekście tej choroby.
„Nasze odkrycia podkreślają złożoną interakcję między TE a układem odpornościowym w kardiomiopatii, dostarczając nowego wglądu w mechanizmy molekularne leżące u podstaw tej choroby” – dodaje Chen.
W szczególności odkrycie specyficznej ekspresji TE w komórkach odpornościowych serca i ogólny wzrost ERVB7-1. Ekspresja LTR-MM w modelu EAM podkreśla potencjał tych elementów w modulowaniu odpowiedzi immunologicznych i przyczynia się do zrozumienia patogenezy kardiomiopatii. Obserwacje te otwierają możliwości dalszych badań nad rolą TE w chorobach serca, optymalizując nowe strategie terapeutyczne.
###
Skontaktuj się z autorem: Yuequn Wang, Centrum Rozwoju Serca, Państwowe Kluczowe Laboratorium Biologii Rozwojowej Ryb Słodkowodnych, College of Life Sciences, Hunan Normal University, yuequnwang@hunnu.edu.cn
Wydawnictwo KeAi zostało założone przez Elsevier i China Science Publishing & Media Ltd w celu rozwijania badań jakości na całym świecie. W 2013 roku skupiliśmy się na publikacjach w otwartym dostępie. Obecnie z dumą publikujemy ponad 100 światowej klasy anglojęzycznych czasopism o otwartym dostępie, obejmujących wszystkie dyscypliny naukowe. Wiele z nich to tytuły, które publikujemy we współpracy z prestiżowymi stowarzyszeniami i instytucjami akademickimi, takimi jak Chińska Narodowa Fundacja Nauk Przyrodniczych (NSFC).
Dziennik
Rozmnażanie i hodowla
Metoda badań
Analiza danych/statystyczna
Przedmiot badań
Próbki tkanek zwierzęcych
Tytuł artykułu
Identyfikacja kluczowych TE związanych z zapaleniem mięśnia sercowego w oparciu o RNA i eksplorację danych sekwencjonowania pojedynczych komórek
Oświadczenie dotyczące COI
Wszyscy autorzy deklarują, że nie mają konkurencyjnych interesów.
Zastrzeżenie: AAAS i EurekAlert! nie odpowiadają za dokładność komunikatów prasowych publikowanych w EurekAlert! przez instytucje wnoszące wkład lub za wykorzystanie jakichkolwiek informacji za pośrednictwem systemu EurekAlert.