Moc małych urządzeń do edycji genomu roślin

Dostarczanie maszyn do edycji genomu do komórek roślinnych pozostaje wyzwaniem, pomimo pilnej potrzeby upraw o wysokiej wydajności i zwiększonej wartości odżywczej, odpornych na choroby i odpornych na zmiany klimatyczne. „Naszym największym problemem jest zmiana klimatu. A największym rozwiązaniem jest CRISPR” — powiedział Rodolphe Barrangou, doktor, profesor na wydziale nauk o żywności, bioprzetwórstwie i żywieniu na North Carolina State University (NCSU) w wywiadzie dla GEN.
Motywowany wyzwaniem opracowania wydajnego i wszechstronnego edytora genomu, który będzie optymalnie działał w komórkach roślinnych, zespół badaczy z ICAR-National Rice Research Institute w Cuttack w Indiach, pod przewodnictwem dr. Kutubuddina Molli i dr. Mirzy Baiga, postanowił wykorzystać enzym transpozazy ISDra2TnpB w bakterii (Deinokok radiodurans) potrafiące przetrwać w ekstremalnych warunkach (ekstremofil).
Grupa Molli i Baiga opublikowała niedawno swoje ustalenia w artykule w Czasopismo biotechnologii roślin„Miniaturowa alternatywa dla Cas9 i Cas12: TnpB powiązany z transpozonem pośredniczy w ukierunkowanej edycji genomu u roślin” we współpracy z Yinong Yang, doktorem, i Justinem Shihem, doktorem, z wydziału fitopatologii i mikrobiologii środowiskowej oraz Huck Institutes of the Life Sciences na Pennsylvania State University.
Efektywność edycji
Badanie twierdzi, że nowy system oparty na TnpB osiąga wydajność edycji na poziomie 33,58% w przeciętnym genomie roślinnym i może celować w regiony genomu, które są niedostępne dla Cas9 lub Cas12. Badanie pokazuje również, że nowy edytor genomu działa w obu typach gatunków roślin kwitnących — tych z jednym lub dwoma „liśćmi nasiennymi” lub liścieniami (jednoliścienne i dwuliścienne), co czyni ISDra2TnpB wszechstronnym i obiecującym narzędziem do inżynierii genomu roślin.
Wcześniejsze badania wykazały skuteczność edytorów genomu opartych na TnpB w komórkach bakterii i ssaków, ale nie zbadały ich zastosowania i skuteczności w roślinach. „Nie wiadomo było, czy TnpB można również wykorzystać do opracowania narzędzi do aktywacji funkcji genu (aktywator) i wymiany liter DNA (edytor zasad) [in the plant genome]— dodała Molla.
Transpozazy TnpB mają długość zaledwie 400–500 aminokwasów (aa) — znacznie mniej niż Cas9 (1000–1500 aa) lub Cas12a (1100–1300 aa), o których uważa się, że wyewoluowały niezależnie od nukleazy podobnej do TnpB. Kompaktowość sprawia, że systemy transpozaz oparte na TnpB są atutem w przypadkach, gdy rozmiar białka lub kwasu nukleinowego jest czynnikiem ograniczającym.
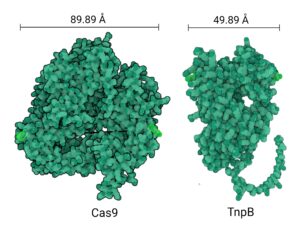
„[This compactness] zapewnia wygodę dostawy za pośrednictwem Agrobakterie-pośredniczona transformacja T-DNA lub poprzez dostawę opartą na wektorach wirusowych”, powiedział Yiping Qi, PhD, profesor na wydziale nauk o roślinach i architektury krajobrazu na University of Maryland. „Ponadto korzystne może być wykorzystanie tych małych białek do opracowania regulacji transkrypcyjnej i narzędzi do edycji epigenomu poprzez fuzję białek”. (Yiping Qi nie brał udziału w tym badaniu).
Podczas gdy Cas9 i Cas12 wymagają obecności 2–6 par zasad PAM (motyw sąsiadujący z protospacerem) do przecięcia dwuniciowego DNA, rozszczepienie przez TnpB zależy od obecności TAM (motywu związanego z transpozonem) przed sekwencją docelową. Analiza całego genomu podkreśla zwiększoną celowalność TnpB w porównaniu z nukleazami Cas. Motyw TAM zapewnia również systemowi TnpB wysoki stopień specyficzności.
„TnpB jest wysoce specyficzny dla swojego motywu (TTGAT). Zbadaliśmy zmianę pojedynczej litery w tym motywie i nie znaleźliśmy żadnego lub nieistotnego rozszczepienia” – powiedział Molla.
![Autorami niniejszego badania są (pierwszy rząd, od lewej do prawej) analityczki danych Priya Das i Debasmita Panda, główni badacze dr Mirza Baig i dr Kutubuddin Molla oraz Manaswini Das, Sonali Panda i SP Avinash; (tylny rząd, od lewej do prawej) dr Romio Saha i dr Subhasis Karmakar, którzy przyczynili się do eksperymentów i analizy danych. [Kutubuddin Molla, PhD].[](https://oen.pl/wp-content/uploads/2024/07/1721349528_374_Moc-malych-urzadzen-do-edycji-genomu-roslin.jpeg)
W tym badaniu naukowcy wykazali skuteczność systemu opartego na TnpB zarówno w aktywacji genów, jak i edycji zasad w genomie roślin. Katalitycznie martwy TnpB wykorzystany w systemie wprowadza specyficzne zmiany pojedynczych nukleotydów bez pęknięć dwuniciowych.
Qi dodał: „Można wprowadzić ulepszenia, które jeszcze bardziej zwiększą wydajność edycji tych nukleaz TnpB, a także złagodzą ich wymagania dotyczące TAM, aby poszerzyć zakres docelowy w genomach roślin” – dodał Qi.
ISDra2TnpB potencjalnie może znaleźć wiele zastosowań w ulepszaniu upraw, precyzyjnej hodowli roślin i w opracowywaniu przyjaznych dla środowiska pestycydów biologicznych. Aby ulepszyć uprawy, system TnpB może być używany do wprowadzania lub wzmacniania cech, takich jak zawartość składników odżywczych, plon oraz odporność na suszę i szkodniki.
System TnpB można również wykorzystać do modyfikacji mikrobów, aby zwiększyć ich zdolność do skuteczniejszego atakowania i zabijania konkretnych szkodników. Z drugiej strony system można również wykorzystać do poprawy naturalnych mechanizmów obronnych roślin lub zmniejszenia podatności roślin na szkodniki, zmniejszając potrzebę zewnętrznych środków zwalczania szkodników.
W ramach nadchodzących projektów zespół Molli i Baiga będzie badał i udoskonalał warianty TnpB pochodzące z różnych organizmów, aby rozszerzyć ich zastosowanie w różnych gatunkach roślin.






