Narzędzie analityczne szybko ujawnia różnorodność genetyczną na potrzeby hodowli roślin nowej generacji
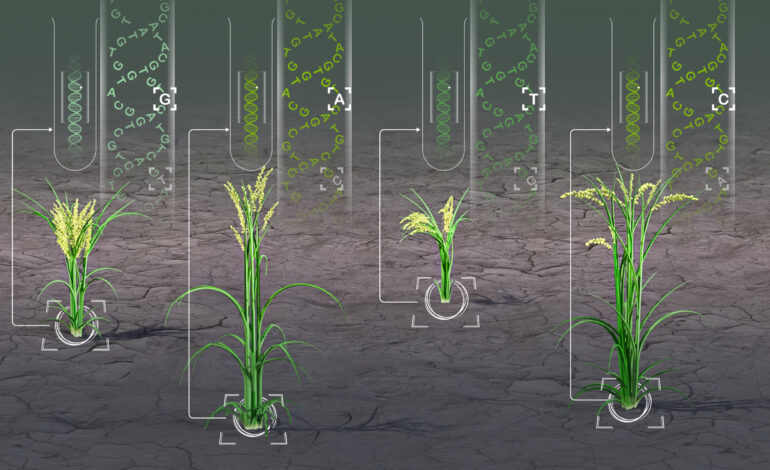
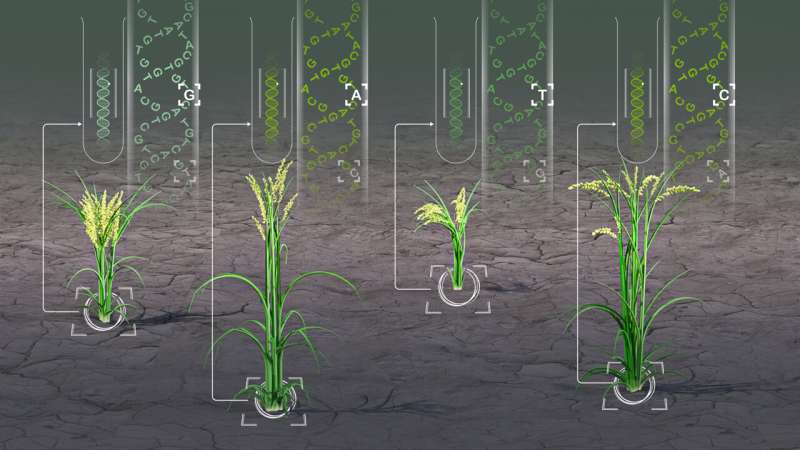
HPC-GVCW to narzędzie obliczeniowe, które szybko identyfikuje różnice genetyczne u kilku gatunków roślin. Pomaga to ulepszyć uprawy, takie jak ryż, kukurydza, soja i sorgo. Źródło: 2024 KAUST; Heno Hwang.
W ramach istotnego postępu w naukach rolniczych badacze opracowali nowe narzędzie obliczeniowe zaprojektowane do szybkiego i skutecznego ujawniania różnorodności genetycznej w bazach danych DNA różnych gatunków roślin.
Platforma typu open source może przyspieszyć odkrywanie zmian genetycznych, które są kluczowe dla uzyskania upraw o zwiększonej odporności, plonach i wartości odżywczej.
Wykorzystując zaawansowane algorytmy i możliwości obliczeń o dużej wydajności (HPC), zespół KAUST, kierowany przez genomika roślin Roda Winga, zademonstrował zdolność narzędzia do wykrywania niewielkich różnic w DNA – tak zwanych wariantów pojedynczego nukleotydu (SNP) – w różnych szczepach ryż, kukurydza, sorgo i sorgo.
Na przykład w przypadku badań nad ryżem zespół zastosował to narzędzie w oparciu o złożony zbiór danych genetycznych obejmujący sekwencje DNA z tysięcy różnych pozycji — kompleksowy „pangenom”, który badacze pomogli wcześniej zebrać dla ryżu azjatyckiego (Oryza sativa).
Wykorzystując ten zbiór danych w połączeniu z nowatorską metodą analityczną opracowaną przez grupę, badacze z projektu KAUST odkryli ponad 2 miliony wariantów genetycznych wcześniej przeoczonych w konwencjonalnych badaniach pojedynczego referencyjnego genomu ryżu.
Oznacza to pierwszy krok w kierunku odblokowania nowych możliwości ulepszania upraw i zrównoważonego rolnictwa, zauważa genetyk roślin i współautor badania Yong Zhou. „Te ukryte SNP można teraz natychmiast wykorzystać w programach hodowlanych, a także do identyfikacji nowych genów funkcjonalnych odpowiedzialnych za cechy rolnicze” – mówi.
Odkrycie SNP w ten sposób może również pomóc w ujawnieniu genetycznych i ewolucyjnych powiązań między różnymi liniami ryżu. Niedawno Wing i Zhou przewodzili tworzeniu wysokiej jakości genomu referencyjnego dla czerwonego ryżu Hassawi, rośliny uprawnej pochodzącej z Arabii Saudyjskiej, znanej ze swojej odporności na lokalną suszę i wysokie zasolenie.
Korzystając z tego narzędzia, badaczom udało się ustalić powiązanie genetyczne między ryżem Hassawi a podgrupą ryżu obejmującą odmiany pochodzące z Australii, Indii i części Azji Południowo-Wschodniej.
Kluczem do wydajności narzędzia — zwanego przepływem pracy wywoływania wariantów genomu o wysokiej wydajności (HPC-GVCW) — jest możliwość podzielenia dużych fragmentów genomu na oddzielne bity, a następnie poleganie na technologiach przetwarzania równoległego w celu rozwiązywania złożonych problemów obliczeniowych na wielkoskalowe, wielowymiarowe dane genomiczne.
„To znacznie skraca czas wykonania” – mówi współautor badania, Nagarajan Kathiresan, informatyk, „dzięki czemu jest w stanie przetworzyć 3000 genomów w ciągu 24 godzin”.
Zhou dodaje, że obecnie sekwencjonuje się więcej genomów niż kiedykolwiek wcześniej, a nowe narzędzie powinno okazać się nieocenione w usprawnianiu analiz i zwiększaniu możliwości hodowli roślin nowej generacji.
Praca publikowana jest w czasopiśmie Biologia BMC.
Więcej informacji:
Yong Zhou i wsp., Wysokowydajny proces obliczeniowy przyspieszający wykrywanie SNP GATK w zestawie danych obejmującym 25 genomów, Biologia BMC (2024). DOI: 10.1186/s12915-024-01820-5
Dostarczone przez Uniwersytet Nauki i Technologii Króla Abdullaha
Cytat: Narzędzie analityczne szybko ujawnia różnorodność genetyczną na potrzeby hodowli roślin nowej generacji (2024, 20 marca) pobrano 20 marca 2024 r. z
Niniejszy dokument podlega prawu autorskiemu. Z wyjątkiem uczciwego obrotu w celach prywatnych studiów lub badań, żadna część nie może być powielana bez pisemnej zgody. Ta zawartość jest w jedynie w celach informacyjnych.






