Prenatalna analiza sekwencjonowania całego genomu (egzomu lub genomu) w wykrywaniu patogennych wariantów pojedynczych nukleotydów w anomaliach centralnego układu nerwowego płodu: przegląd systematyczny i metaanaliza
Barbitoff YA, Polev DE, Glotov AS, Serebryakova EA, Shcherbakova IV, Kiselev AM i in. Systematyczne analizowanie błędów w sekwencjonowaniu całego egzomu i całego genomu ujawnia główne determinanty pokrycia sekwencji kodującej. Republika Nauki 2020;10:2057. https://doi.org/10.1038/s41598-020-59026-y.
Liu P, Vossaert L. Nowe technologie diagnostyki prenatalnej: zastosowanie sekwencjonowania całego genomu i RNA. Diagnoza prenatalna 2022;42:686–96. https://doi.org/10.1002/pd.6146.
Manickam K, McClain MR, Demmer LA, Biswas S, Kearney HM, Malinowski J i in. Sekwencjonowanie egzomu i genomu pacjentów pediatrycznych z wadami wrodzonymi lub niepełnosprawnością intelektualną: oparte na dowodach wytyczne kliniczne American College of Medical Genetics and Genomics (ACMG). Genet Med. 2021;23:2029–37. https://doi.org/10.1038/s41436-021-01242-6.
Guadagnolo D, Mastromoro G, Di Palma F, Pizzuti A, Marchionni E. Prenatalne sekwencjonowanie egzomów: tło, obecna praktyka i przyszłe perspektywy – przegląd systematyczny. Diagnostyka. 2021;11:224. https://doi.org/10.3390/diagnostics11020224.
Van den Veyver IB, Chandler N, Wilkins-Haug LE, Wapner RJ, Chitty LS, Zarząd ISPD. Międzynarodowe Towarzystwo Diagnostyki Prenatalnej Zaktualizowane stanowisko w sprawie stosowania sekwencjonowania całego genomu w diagnostyce prenatalnej. Diagnoza prenatalna 2022;42:796–803. https://doi.org/10.1002/pd.6157.
Wang Y, Greenfeld E, Watkins N, Belesiotis P, Zaidi SH, Marshall C i in. Wydajność diagnostyczna sekwencjonowania genomu w diagnostyce prenatalnej anomalii strukturalnych płodu. Diagnoza prenatalna 2022;42:822–30. https://doi.org/10.1002/pd.6108.
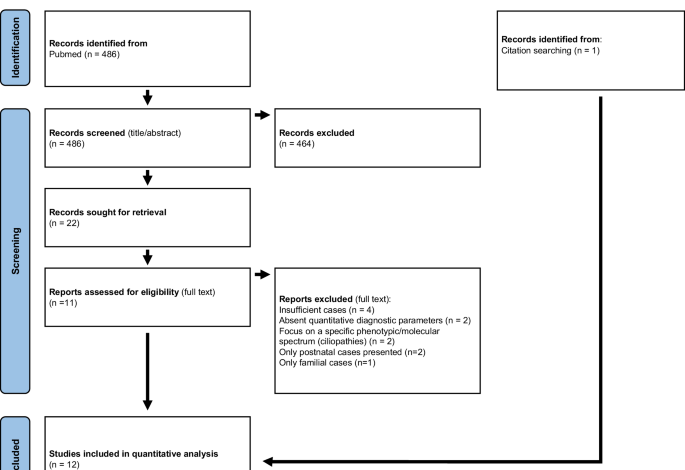
Page MJ, McKenzie JE, Bossuyt PM, Boutron I, Hoffmann TC, Mulrow CD i in. Oświadczenie PRISMA 2020: zaktualizowane wytyczne dotyczące raportowania przeglądów systematycznych. BMJ. 2021;372:n71. https://doi.org/10.1136/bmj.n71.
Munn Z, Barker TH, Moola S, Tufanaru C, Stern C, McArthur A i in. Jakość metodologiczna badań serii przypadków: wprowadzenie do narzędzia krytycznej oceny JBI. Syntezator JBI Evid. 2020;18:2127–33. https://doi.org/10.11124/JBISRIR-D-19-00099.
Yaron Y, Ofen Glassner V, Mory A, Zunz Henig N, Kurolap A, Bar Shira A i in. Sekwencjonowanie egzomu jako badanie pierwszego stopnia u płodów z poważnymi anomaliami strukturalnymi ośrodkowego układu nerwowego. USG Obstet Gynecol. 2022;60:59–67. https://doi.org/10.1002/uog.24885.
Lei TY, She Q, Fu F, Zhen L, Li R, Yu QX i in. Prenatalne sekwencjonowanie egzomu u płodów z anomaliami modzelowatymi. Diagnoza prenatalna 2022;42:744–52. https://doi.org/10.1002/pd.6107.
de Koning MA, Hoffer MJV, Nibbeling EAR, Bijlsma EK, Toirkens MJP, Adama-Scheltema PN i in. Prenatalne sekwencjonowanie egzomu: przydatne narzędzie dla neurologa płodu. Clina Geneta. 2022;101:65–77. https://doi.org/10.1111/cge.14070.
She Q, Tang E, Peng C, Wang L, Wang D, Tan W. Prenatalne badania genetyczne u 19 płodów z nieprawidłowością ciała modzelowatego. Anal laboratoryjny J Clin. 2021;35:e23971. https://doi.org/10.1002/jcla.23971.
Heide S, Spentchian M, Valence S, Buratti J, Mach C, Lejeune E i in. Prenatalne sekwencjonowanie egzomu u 65 płodów z nieprawidłowością ciała modzelowatego: wkład w dalsze określenie diagnostyki. Genet Med. 2020;22:1887–91. https://doi.org/10.1038/s41436-020-0872-8.
Tan H, Xie Y, Chen F, Chen M, Yu L, Chen D i in. Nowe i nawracające warianty zidentyfikowane u płodów z nieprawidłowościami w ośrodkowym układzie nerwowym za pomocą sekwencjonowania egzomów metodą trios-medyczną. Clin Chim Acta. 2020;510:599–604. https://doi.org/10.1016/j.cca.2020.08.018.
Li L, Fu F, Li R, Xiao W, Yu Q, Wang D i in. Badania genetyczne pomagają w poradnictwie dla płodów z wadami robaka móżdżku. Diagnoza prenatalna 2020;40:1228–38. https://doi.org/10.1002/pd.5732.
Weitensteiner V, Zhang R, Bungenberg J, Marks M, Gehlen J, Ralser DJ i in. Sekwencjonowanie egzomu w syndromicznych malformacjach mózgu pozwala zidentyfikować nowe mutacje w ACTB i SLC9A6 oraz sugeruje BAZ1A jako nowy gen kandydujący. Wady wrodzone Res. 2018;110:587–97. https://doi.org/10.1002/bdr2.1200.
Reches A, Hiersch L, Simchoni S, Barel D, Greenberg R, Ben Sira L i in. Sekwencjonowanie całego egzomu u płodów z nieprawidłowościami w ośrodkowym układzie nerwowym. J Perinatol. 2018;38:1301–8. https://doi.org/10.1038/s41372-018-0199-3.
Poirier K, Martinovic J, Laquerrière A, Cavallin M, Fallet-Bianco C, Desguerre I i in. Rzadkie warianty ACTG1 w mikrolisencefalii płodowej. Eur J Med Genet. 2015;58:416–8. https://doi.org/10.1016/j.ejmg.2015.06.006.
Liao Y, Yang Y, Wen H, Wang B, Zhang T, Li S. Nieprawidłowa szczelina Sylviana w 20–30 tygodniu jako wskaźnik wad rozwojowych rozwoju kory: rola prenatalnego sekwencjonowania całego genomu. USG Obstet Gynecol. 2022;59:552–5. https://doi.org/10.1002/uog.24771.
Yang Y, Zhao S, Sun G, Chen F, Zhang T, Song J i in. Architektura genomowa anomalii ośrodkowego układu nerwowego płodu przy użyciu sekwencjonowania całego genomu. NPJ Genom Med. 2022;7:31 Opublikowano 2022 13 maja.
Baujat B, Mahé C, Pignon JP, Hill C. Graficzna metoda badania heterogeniczności w metaanalizach: zastosowanie do metaanalizy 65 badań. Stat Med. 2002;21:2641–52. https://doi.org/10.1002/sim.1221.
Balduzzi S, Rücker G, Schwarzer G. Jak przeprowadzić metaanalizę za pomocą R: poradnik praktyczny. Zdrowie psychiczne oparte na dowodach. 2019;22:153–60. https://doi.org/10.1136/ebmental-2019-300117.
Harrer M, Cuijpers, Furukawa T, Ebert DD. Dmetar: Pakiet Companion R do przewodnika „Przeprowadzanie metaanalizy w R”. Wersja pakietu R 0.0.9000. 2019. http://dmetar.protectlab.org/.
Lord J, McMullan DJ, Eberhardt RY, Rinck G, Hamilton SJ, Quinlan-Jones E i in. Prenatalna analiza sekwencjonowania egzomu w anomaliach strukturalnych płodu wykrytych za pomocą ultrasonografii (PAGE): badanie kohortowe. Lancet. 2019;393:747–57. https://doi.org/10.1016/S0140-6736(18)31940-8.
Petrovski S, Aggarwal V, Giordano JL, Stosic M, Wou K, Bier L i in. Sekwencjonowanie całego egzomu w ocenie anomalii strukturalnych płodu: prospektywne badanie kohortowe. Lancet. 2019;393:758–67. https://doi.org/10.1016/S0140-6736(18)32042-7.
Mellis R, Oprych K, Scotchman E, Hill M, Chitty LS. Wydajność diagnostyczna sekwencjonowania egzomu w diagnostyce prenatalnej anomalii strukturalnych płodu: przegląd systematyczny i metaanaliza. Diagnoza prenatalna 2022;42:662–85. https://doi.org/10.1002/pd.6115.
Międzynarodowe Towarzystwo Diagnostyki Prenatalnej; Towarzystwo Medycyny Matczynej i Płodowej; Fundacja Jakości Perinatalnej. Wspólne stanowisko Międzynarodowego Towarzystwa Diagnostyki Prenatalnej (ISPD), Towarzystwa Medycyny Płodu Matczynego (SMFM) i Fundacji Jakości Perinatalnej (PQF) w sprawie stosowania sekwencjonowania całego genomu w diagnostyce płodu. Diagnoza prenatalna 2018;38:6–9. https://doi.org/10.1002/pd.5195.
Monaghan KG, Leach NT, Pekarek D, Prasad P, Rose NC, Komisja ds. Praktyki Zawodowej i Wytycznych ACMG. Zastosowanie sekwencjonowania egzomu płodu w diagnostyce prenatalnej: dokument Amerykańskiego Kolegium Genetyki Medycznej i Genomiki (ACMG), który należy wziąć pod uwagę. Genet Med. 2020;22:675–80. https://doi.org/10.1038/s41436-019-0731-7.
Mustafa HJ, Barbera JP, Sambatur EV, Pagani G, Yaron Y, Baptiste CD i in. Wydajność diagnostyczna sekwencjonowania egzomu w prenatalnej agenezie ciała modzelowatego: przegląd systematyczny i metaanaliza. USG Obstet Gynecol. 2023. https://doi.org/10.1002/uog.27440.
Hart AR, Vasudevan C, Griffiths PD, Foulds N, Piercy H, de Lacy P i in. Poradnictwo przedporodowe dla przyszłych rodziców, których płód ma anomalię neurologiczną: część 2, ryzyko niekorzystnych wyników w przypadku typowych anomalii. Dev Med Child Neurol. 2022;64:23–39. https://doi.org/10.1111/dmcn.15043.
Mone F, Abu Subieh H, Doyle S, Hamilton S, Mcmullan DJ, Allen S i in. Ewoluujące fenotypy płodów i wpływ kliniczny postępujących szlaków prenatalnego sekwencjonowania egzomów: badanie kohortowe. USG Obstet Gynecol. 2022;59:723–30. https://doi.org/10.1002/uog.24842.
Giordano JL, Wapner RJ. Konsorcjum zajmujące się sekwencjonowaniem płodu: wartość interdyscyplinarnego dialogu i współpracy. Diagnoza prenatalna 2022;42:807–10. https://doi.org/10.1002/pd.6190.
Chandler NJ, Scotchman E, Mellis R, Ramachandran V, Roberts R, Chitty LS. Wnioski wyciągnięte z prenatalnego sekwencjonowania egzomu. Diagnoza prenatalna 2022;42:831–44. https://doi.org/10.1002/pd.6165.
Miller DT, Lee K, Abul-Husn NS, Amendola LM, Brothers K, Chung WK i in. Lista ACMG SF v3.2 do zgłaszania wtórnych ustaleń w sekwencjonowaniu egzomu klinicznego i genomu: oświadczenie polityczne American College of Medical Genetics and Genomics (ACMG). Genet Med. 2023;25:100866. https://doi.org/10.1016/j.gim.2023.100866.
Brew CE, Castro BA, Pan V, Hart A, Blumberg B, Wicklund C. Postawy specjalistów z zakresu genetyki wobec prenatalnego sekwencjonowania egzomów. J. Genet Couns. 2019;28:229–39. https://doi.org/10.1002/jgc4.1112.
Vaknin N, Azoulay N, Tsur E, Tripolszki K, Urzi A, Rolfs A i in. Wysoki odsetek nieprawidłowych wyników badania Prenatal Exome Trio w ciążach niskiego ryzyka i pozornie prawidłowych płodach. Diagnoza prenatalna 2022;42:725–35. https://doi.org/10.1002/pd.6077.
Wang H, Dong Z, Zhang R, Chau MHK, Yang Z, Tsang KYC i in. Dolnoprzepustowe sekwencjonowanie genomu a analiza mikromacierzy chromosomowych: zastosowanie w diagnostyce prenatalnej. Genet Med. 2020;22:500–10. https://doi.org/10.1038/s41436-019-0634-7.
Stranneheim H, Lagerstedt-Robinson K, Magnusson M, Kvarnung M, Nilsson D, Lesko N i in. Integracja sekwencjonowania całego genomu w środowisku opieki zdrowotnej: wysokie wskaźniki diagnostyczne w wielu jednostkach klinicznych u 3219 pacjentów z rzadkimi chorobami. Genom Med 2021;13:40. https://doi.org/10.1186/s13073-021-00855-5.