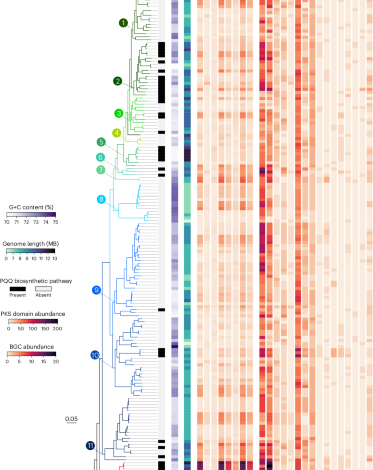
Wyjaśnienie genów wzmacniających biosyntezę produktów naturalnych poprzez analizę koewolucji
Newman, DJ & Cragg, GM Produkty naturalne jako źródła nowych leków na przestrzeni prawie czterdziestu lat od 01.1981 do 09.2019. J. Nat. Szturchać. 83770–803 (2020).
Li, S., Li, Z., Pang, S., Xiang, W. & Wang, W. Koordynacja dostaw prekursorów do produkcji poliketydów farmaceutycznych w Streptomyces. Aktualny Opinia. Biotechnologia. 6926–34 (2021).
Wang, W. i in. Wykorzystanie wewnątrzkomórkowych triacylogliceroli do poprawy miana poliketydów w Streptomyces. Nat. Biotechnologia. 3876–83 (2020).
Liu, G., Chater, KF, Chandra, G., Niu, G. & Tan, H. Molekularna regulacja biosyntezy antybiotyków w Streptomyces. Mikrobiol. Mol. Biol. Obrót silnika. 77112–143 (2013).
Gavriilidou, A. i in. Kompendium różnorodności biosyntezy wyspecjalizowanych metabolitów zakodowanej w genomach bakterii. Nat. Mikrobiol. 7726–735 (2022).
Gao, L. i in. Pan-genom pomidora odkrywa nowe geny i rzadki allel regulujący smak owoców. Nat. Geneta. 511044–1051 (2019).
de Vriesa, RP i in. Genomika porównawcza ujawnia wysoką różnorodność biologiczną i specyficzne adaptacje w rodzaju grzybów ważnych pod względem przemysłowym i medycznym Aspergillus. Biol genomu. 1828 (2017).
Cruz-Morales, P. i in. Ponowny przegląd ewolucji i taksonomii Clostridia, aktualizacja filogenomiczna. Biol genomu. Ewolucja 112035–2044 (2019).
Chandra, G. i Chater, KF Biologia rozwojowa Streptomyces z perspektywy 100 sekwencji genomu promieniowców. Mikrobiolog FEMS. Obrót silnika. 38345–379 (2014).
Schoch, CL i in. Taksonomia NCBI: kompleksowa aktualizacja dotycząca selekcji, zasobów i narzędzi. Baza danych (2020).
Bentley, SD i in. Pełna sekwencja genomu modelowego promieniowca Streptomyces coelicolor A3(2). Natura 417141–147 (2002).
Kim, JN i in. Genomika porównawcza ujawnia genomy rdzeniowe i dodatkowe Streptomyces gatunek. J. Mikrobiol. Biotechnologia. 251599–1605 (2015).
Bu, QT i in. Kompleksowa sekcja zbędnych regionów genomowych w Streptomyces w oparciu o podejście analizy porównawczej. Mikro. Fakt komórkowy. 1999 (2020).
Zhou, Z., Gu, J., Li, YQ i Wang, Y. Plastyczność genomu i ewolucja systemów w Streptomyces. BMC Bioinf. 13S8 (2012).
Belknap, KC, Park, CJ, Barth, BM i Andam, CP Eksploracja genomu klastrów genów biosyntetycznych i chemioterapeutycznych w Streptomyces bakteria. Nauka. Reprezentant. 102003 (2020).
Zaburannyi, N., Rabyk, M., Ostash, B., Fedorenko, V. i Luzhetskyy, A. Wgląd w naturalnie zminimalizowane Streptomyces albus Genom J1074. Gen BMC. 1597 (2014).
Chung, YH i in. Genomika porównawcza ujawnia niezwykły potencjał biosyntetyczny Streptomyces linia filogenetyczna związana z zarodnikami ozdobionymi rugozą. mSystemy 6e0048921 (2021).
Jonscher, KR, Chowanadisai, W. i Rucker, RB Pirolochinolinochinon to coś więcej niż przeciwutleniacz: podobny do witaminy czynnik dodatkowy ważny w zapobieganiu zdrowiu i chorobom. Biocząsteczki 111441 (2021).
Wagh, J., Shah, S., Bhandari, P., Archana, G. i Kumar, GN Heterologiczna ekspresja klastra genów pirolochinolinochinonu (PQQ) nadaje zdolność solubilizacji fosforanów mineralnych Herbaspirillum seropedicae Z67. Aplikacja Mikrobiol. Biotechnologia. 985117–5129 (2014).
Zhu, W. i Klinman, JP Biogeneza pirolochinoliny, kofaktora redoks pochodzącego z peptydu. Aktualny Opinia. Chem. Biol. 5993–103 (2020).
Shen, YQ i in. Rozmieszczenie i właściwości genów kodujących biosyntezę kofaktora bakteryjnego, chinonu pirolochinoliny. Biochemia 512265–2275 (2012).
Yamauchi, Y. i in. Dehydrogenaza chinoproteinowa działa na ostatnim etapie utleniania biosyntezy lankacydyny Streptomyces rochei 7434AN4. J. Biosci. Bioeng. 126145–152 (2018).
Cruz-Morales, P. i in. Biosynteza policyklopropanowanych biopaliw wysokoenergetycznych. Dżul 61590–1605 (2022).
Moumbock, AFA i in. StreptomeDB 3.0: zaktualizowane kompendium naturalnych produktów streptomycetes. Kwasy nukleinowe Res. 49D600–D604 (2021).
Olano, C. i in. Aktywacja i identyfikacja pięciu klastrów metabolitów wtórnych w Streptomyces albus J1074. Mikrob. Biotechnologia. 7242–256 (2014).
Xu, F., Nazari, B., Moon, K., Bushin, LB i Seyedsayamdost, MR Odkrycie tajemniczego związku przeciwgrzybiczego z Streptomyces albus J1074 wykorzystujący ekrany elicytorowe o dużej przepustowości. J. Am. Chem. Towarzystwo 1399203–9212 (2017).
Beganovic, S. i in. Biologia systemowa przemysłowej produkcji oksytetracykliny w Streptomyces rimosus: sekrety zmutowanego hiperproducenta. Mikrob. Fakt komórkowy. 22222 (2023).
Abbate, E. i in. Optymalizacja procesu inżynierii szczepów na potrzeby produkcji cząsteczek pochodzenia biologicznego na skalę przemysłową. J. Ind. Microbiol. Biotechnologia. 50kuad025 (2023).
Sun, F., Xu, S., Jiang, F. i Liu, W. Odkrycie amidynohydrolazy na podstawie genomu zaangażowanej w biosyntezę mediomycyny A. Aplikacja Mikrobiol. Biotechnologia. 1022225–2234 (2018).
Whitford, CM, Cruz-Morales, P., Keasling, JD i Weber, T. Cykl projektowania-budowy-testowania-uczenia się w zakresie inżynierii metabolicznej Streptomycetes. Eseje Biochem. 65261–275 (2021).
Chen, X. i in. Nowy bakteryjny tRNA zwiększa produkcję antybiotyków Streptomyces poprzez obejście nieefektywnego parowania zasad wahliwych. Kwasy nukleinowe Res. 507084–7096 (2022).
Gessner, A. i in. Zmiana profili biosyntetycznych poprzez ekspresję bldA w Streptomyces szczepy. Chem. Bio. Chem. 162244–2252 (2015).
Tsunematsu, Y. i in. Odrębne mechanizmy tworzenia spiro-węgla ujawniają przesłuchy szlaków biosyntezy. Nat. Chem. Biol. 9818–825 (2013).
Saihara, K., Kamikubo, R., Ikemoto, K., Uchida, K. i Akagawa, M. Pyrrolochinoliny chinon, o-chinon o aktywności redoks, stymuluje biogenezę mitochondriów poprzez aktywację szlaku sygnalizacyjnego SIRT1/PGC-1alfa. Biochemia 566615–6625 (2017).
Simao, FA, Waterhouse, RM, Ioannidis, P., Kriventseva, EV i Zdobnov, EM BUSCO: ocena składania genomu i kompletności adnotacji za pomocą ortologów jednokopiowych. Bioinformatyka 313210–3212 (2015).
Chaudhari, NM, Gupta, VK i Dutta, C. BPGA — ultraszybki potok analizy pangenomu. Nauka. Reprezentant. 624373 (2016).
Minh, BQ i in. IQ-TREE 2: nowe modele i wydajne metody wnioskowania filogenetycznego w erze genomu. Mol. Biol. Ewolucja 371530–1534 (2020).
Blin, K. i in. antiSMASH 6.0: ulepszone możliwości wykrywania i porównywania klastrów. Kwasy nukleinowe Res. 49W29–W35 (2021).
Komaki, H. i Tamura, T. Reklasyfikacja Streptomyces cynamonowy jako późniejszy heterotypowy synonim Streptomyces Virginia. Wewnętrzne J. System. Ewolucja Mikrobiol. 71004813 (2021).
Wang, XR, Wang, RF, Kang, QJ i Bai, LQ Środek przeciwnowotworowy anzamitocyna P-3 wiąże się z białkiem podziału komórkowego FtsZ w Actinosynnema pretiosum. Biocząsteczki 10699 (2020).
Wu, M. i in. Fosfoproteomika odkrywa nowe cele i sieci fosfoproteinowe w cyklu komórkowym, w którym pośredniczy kinaza Dsk1. J. Proteome Res. 191776–1787 (2020).
Zhao, Y., Xiang, S., Dai, X. i Yang, K. Uproszczona metoda kolorymetryczna difenyloaminy do ilościowego oznaczania wzrostu. Aplikacja Mikrobiol. Biotechnologia. 975069–5077 (2013).
Nanchen, A., Fuhrer, T. i Sauer, U. Oznaczanie współczynników strumienia metabolicznego na podstawie eksperymentów 13C i danych z chromatografii gazowej i spektrometrii mas (Człowiek, 2007).