Złamanie kodu 6mA w celu zwiększenia akumulacji lipidów
obraz:
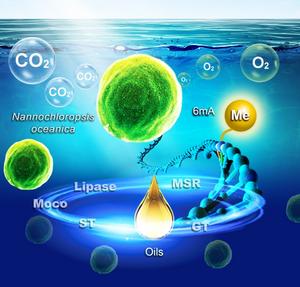
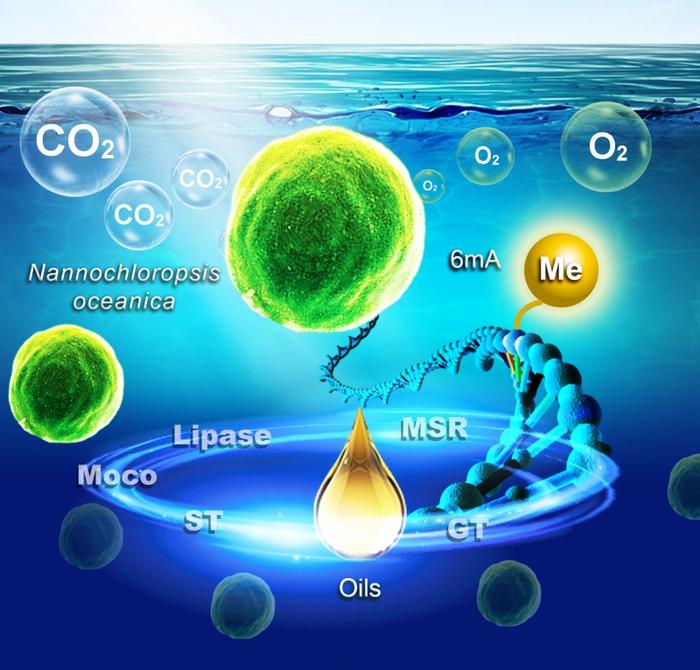
N6-metyloadenozyna (6mA) Modyfikacje metylacyjne 6mA regulują akumulację lipidów w Nannochloropsis oceanica.
pogląd więcej
Źródło: QIBEBT
Mikroalgi, które wnoszą główny wkład w globalną fotosyntezę i pierwotną produktywność, służą jako obiecujące komórki podwozia w biologii syntetycznej.
W badaniu opublikowanym w Komunikacja roślinnabadacze z Instytutu Bioenergii i Technologii Bioprocesów w Qingdao (QIBEBT) Chińskiej Akademii Nauk odkryli wzór dystrybucji i dynamiczne zmiany w DNA N6-metyloadeniny (6mA) w rozdzielczości jednozasadowej w szczepach zmutowanych typu dzikiego i zmutowanych 6mA , ujawniając w ten sposób jego kluczową rolę w akumulacji lipidów, szczególnie w warunkach silnego oświetlenia.
Nannochloropsis oceanica, znana ze swojej wytrzymałości i wydajności w uprawie na wolnym powietrzu, oferuje takie zalety, jak szybki wzrost, silna tolerancja na dwutlenek węgla, silna synteza lipidów i wysokiej jakości nienasycone kwasy tłuszczowe. Dzięki niewielkiemu rozmiarowi genomu (~30 Mb) i haploidalnemu charakterowi pozwala na elastyczną manipulację genetyczną, w tym nokaut genów, nadekspresję, delecję dużych fragmentów genomu i rekombinację homologiczną, z wysoką wydajnością edycji.
6mA jest ważną modyfikacją metylacji DNA. Korzystając z sekwencjonowania w czasie rzeczywistym pojedynczej cząsteczki, badacze ujawnili krajobraz 6 mA całego genomu Nannochloropsis oceanica. Wyniki podkreślają preferencyjne wzbogacenie 6mA w motywie AGGYV, podwyższone poziomy w transpozonach i nieulegających translacji regionach 3′ oraz ścisły związek z aktywną transkrypcją.
„Zaobserwowaliśmy stopniowy wzrost o 6 mA wzdłuż kierunku transkrypcji genu, ze specyficznym wzbogaceniem w pobliżu dawców splicingu i miejsc terminacji transkrypcji” – powiedział GONG Yanhai, współpierwszy autor badania.
Ponadto geny o wysokiej ekspresji wykazują większą liczebność 6 mA w genomie w porównaniu z genami o niskiej ekspresji, co sugeruje pozytywną zależność między 6 mA a ogólnymi czynnikami transkrypcyjnymi.
Aby dokładniej zbadać wpływ prądu 6 mA, naukowcy wyeliminowali gen metylotransferazy 6 mA (NO08G00280). Spowodowało to zmianę wzorców metylacji i zmiany w ekspresji kluczowych genów związanych z kofaktorem molibdenu, transporterami siarczanów, transferazą glikozylową, lipazą i reduktazą sulfotlenku metioniny, ostatecznie prowadząc do zmniejszenia produkcji biomasy i oleju.
I odwrotnie, nokaut genu demetylazy (NO06G02500) spowodował zwiększenie poziomu 6 mA i spowolnienie wzrostu.
„Odkrycia te nie tylko potwierdziły obecność kluczowych enzymów na szlaku regulacji epigenetycznej, ale także rzuciły światło na kluczową rolę 6 mA w akumulacji lipidów w organizmie człowieka. Nannochloropsa w warunkach silnego oświetlenia” – powiedział prof. WANG Qintao, współpierwszy autor badania.
Odkrycia te dostarczają wiedzy na temat wykorzystania epigenetycznych modyfikacji genomu w celu zwiększenia wydajności biomasy i produkcji lipidów w mikroalgach przemysłowych. Badanie jest częścią inicjatywy Nannochloropsis Design & Synthesis Initiative (NanDeSyn), w której uczestniczy 26 zespołów badawczych z ośmiu krajów, koordynujących wysiłki mające na celu postęp w badaniach nad hodowlą molekularną i biologią syntetyczną w zakresie przemysłowych mikroalg wiążących węgiel i wytwarzających ropę.
„Dzięki naszym wspólnym wysiłkom swobodnie udostępnialiśmy kompleksowe zbiory danych, które obejmują mapy modyfikacji epigenetycznych 6 mA całego genomu, transkryptomy i powiązane mutanty w różnych warunkach hodowli. Te cenne zasoby są teraz dostępne dla społeczności naukowej za pośrednictwem strony internetowej NanDeSyn. Nasze wspólne celem jest postęp w badaniach nad mikroalgami przemysłowymi poprzez promowanie wymiany zasobów plazmy zarodkowej, narzędzi genetycznych i informacji z zakresu genomiki funkcjonalnej” – powiedział prof. XU Jian, korespondent autor badania.
Dziennik
Komunikacja roślinna
Metoda badań
Badania eksperymentalne
Przedmiot badań
Nie dotyczy
Tytuł artykułu
Mapa metylacji adeniny N6 obejmująca cały genom ujawnia epigenomiczną regulację akumulacji lipidów u Nannochloropsis
Data publikacji artykułu
24-lis-2023
Zastrzeżenie: AAAS i EurekAlert! nie odpowiadają za dokładność komunikatów prasowych publikowanych w EurekAlert! przez instytucje wnoszące wkład lub za wykorzystanie jakichkolwiek informacji za pośrednictwem systemu EurekAlert.






